VMDでMDシミュレーションのトラジェクトリ の変換とアライン
概要
シミュレーション中の原子の軌跡を保存するトラジェクトリ ファイルの種類が多く混乱したのでメモする。さらに、トラジェクトリ の拡張子を変換しつつ人にとって見やすいようにタンパク質でアライン(中心に固定して動かなくする)する。
環境
macOS Mojave 10.14.6
vmd 1.9.3
トラジェクトリ の種類
トラジェクトリ の種類はシミュレーションソフトによって違うらしい。基本的に互換性がないので、解析するソフトに合わせて適宜変換してあげる必要がある。
| シミュレーションソフト | 拡張子 | 備考 |
|---|---|---|
| GROMACS | xtc | 時間、座標 |
| GROMACS | trr | 時間、座標、速度 |
| Amber | mdcrd | 時間、座標、その他(速度、力、、、) |
| CHARMM, NAMD | dcd | 時間、座標、その他(速度、力、、、) |
他にも多くのトラジェクトリ の種類があるが今回は割愛する。
トラジェクトリ の変換とアライン
GUIとCUI(スクリプト)の方法がある。いづれも以下の手順で行う。
- タンパク質をアライン。
- トラジェクトリ を変換する。
GUIでの方法
まずは構造ファイルとトラジェクトリ ファイルを読み込む。読み込み方はこちら → VMDの使い方の基本 (Mac)
タンパク質でアライン
VMD MainのExtensions=>Analysis=>RMSD Trajectory Tools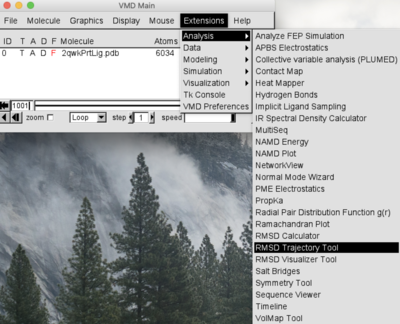
RMSD Trajectory Toolメニューの空白部分でアラインする原子を選択する。図のようにproteinとしSelection Mofidiersのnohにチェックをつけるか、protein and nohとする。その後、ALIGNをクリックする。
トラジェクトリ の変更
VMD Mainで変換したい分子を選択し、右クリック
==>Save Cordinates
Save Trajectoryメニューが出てくる。詳細を設定する。今回はフレーム0番目が構造ファイル、1番目が0nsの構造だったので保存するときは2フレーム目からにした。Save data from: 保存したいデータがあるファイル。Selected atoms: 保存したい原子の選択。入力形式はGraphical RepresentationsのSelected Atomsと同じ。デフォルトは全ての原子。File type: ここで変換したい拡張子を選択。Frames: フレームの最初、最後、間隔を指定。

Saveをクリックして、保存するファイルの名前を入力する。
CUI(スクリプト)での方法
スクリプトの基本はこちら→VMDのスクリプトの書き方
今回は、test.pdbとtest.xtcを読み込んでアラインし、フレーム2番目から最後までをtest.dcdに保存する自動スクリプトを例に示す。
mol load pdb test.pdb xtc test.xtc set num_frame [molinfo top get numframes] set ref [atomselect top "protein and noh" frame 0] for {set i 1} {$i < $num_frame} {incr i} { set all [atomselect top all frame $i] set prt [atomselect top "protein and noh" frame $i] $all move [measure fit $prt $ref] } animate write dcd test.dcd beg 2 exit
手順は以下の通り
- 構造、トラジェクトリファイルを読み込む
- トラジェクトリファイルのフレーム数を取り出す
- 一番最初のフレームのタンパク質情報を取り出す(このタンパク質に合わせて各フレームをアラインする)
- 各フレームの全原子をタンパク質でアラインする
- 2番目のフレームから最後までのフレームを拡張子.dcdとして保存
animateコマンドの詳細はこちら↓
https://www.ks.uiuc.edu/Research/vmd/current/ug/node121.html